具体步骤
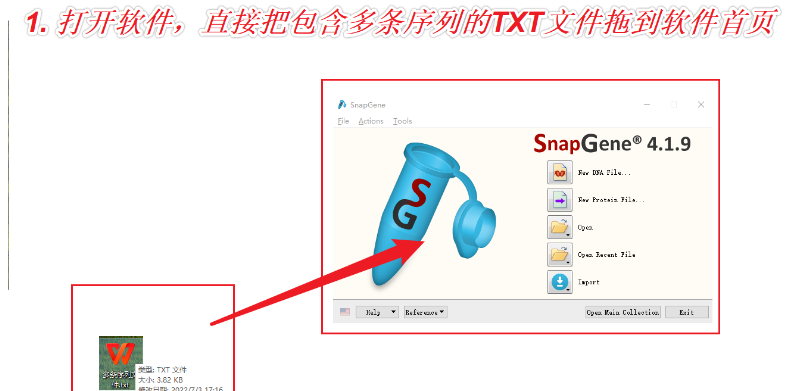
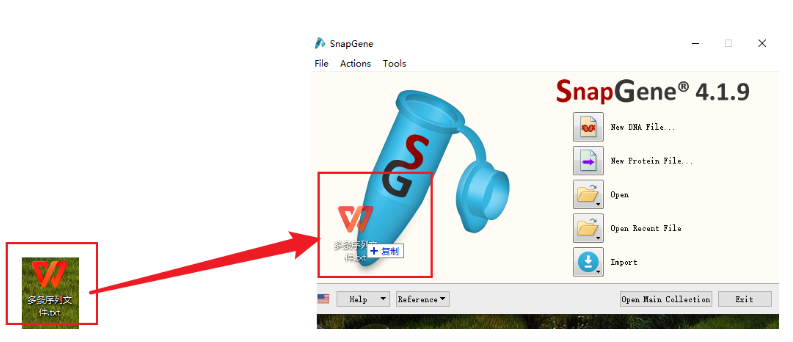
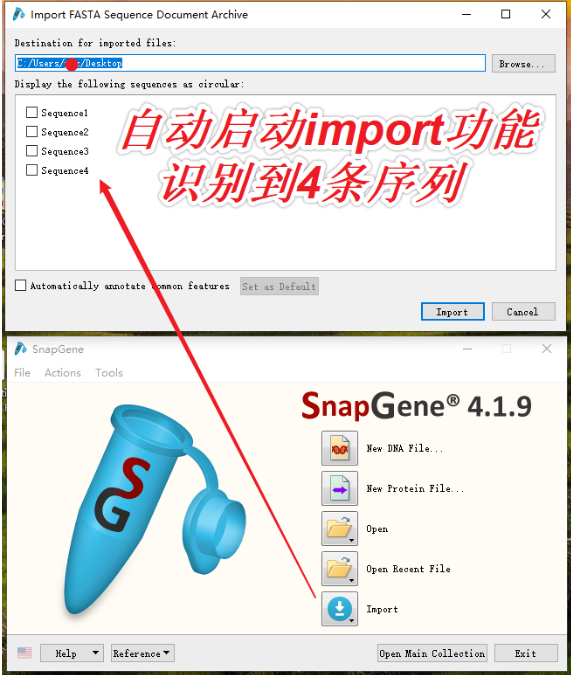
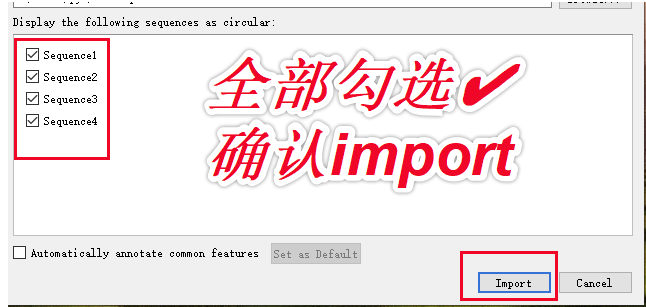
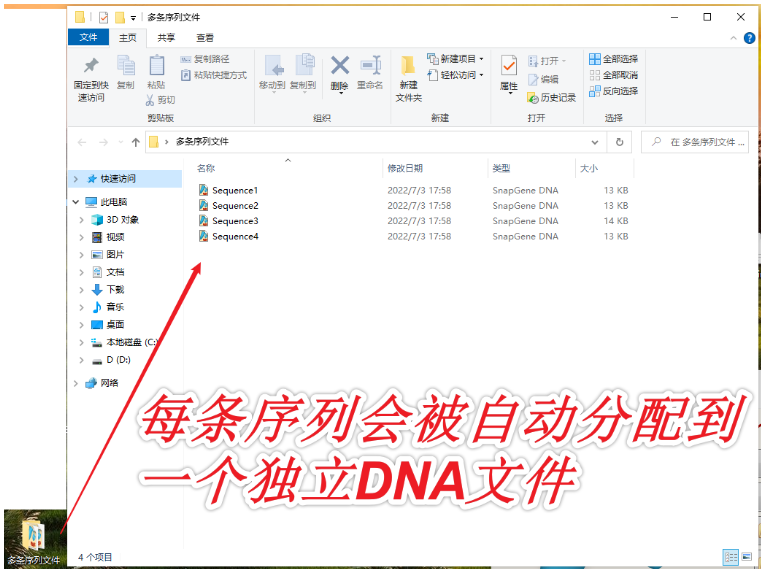
1.打开SnapGene软件,将txt文件拖入软件起始界面。SnapGene将自动识别txt中的每条序列,并将它们拆分成为单独的序列文件,点击“Import”,SnapGene将生成一个文件夹,文件夹中含有txt中的每一个FASTA序列。保存位置看默认设置。
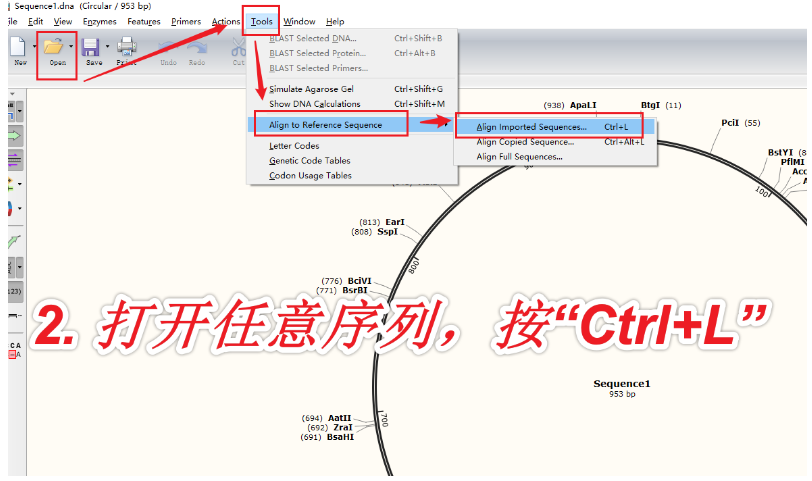
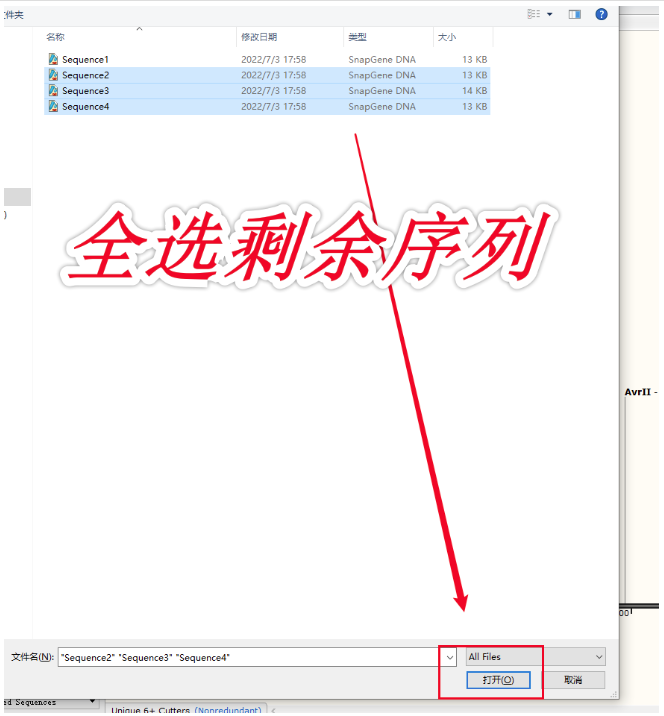
2. 打开任意一个序列,按快捷键Ctrl+L(=菜单栏Tools-Align to Reference Sequences-Align Imported Sequence...),在弹出的窗口中,将剩下几个序列都选中,点击“打开”。依次查看Map、Sequence标签页。

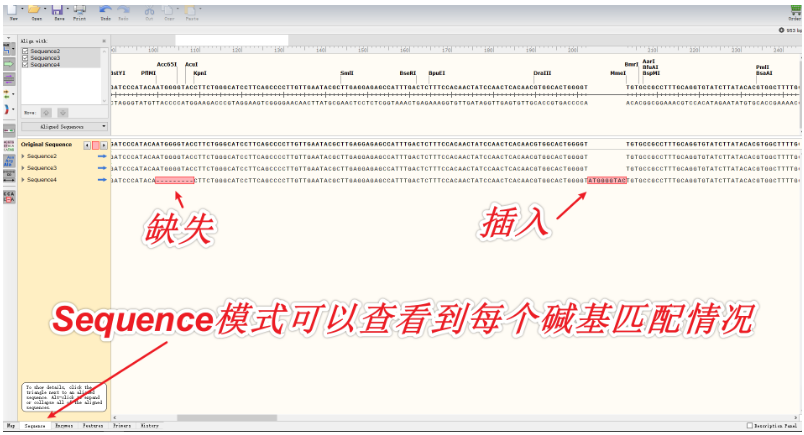
备注:如果序列差别太大也可能匹配不上。
以下介绍质粒或DNA产物测序结果分析方法
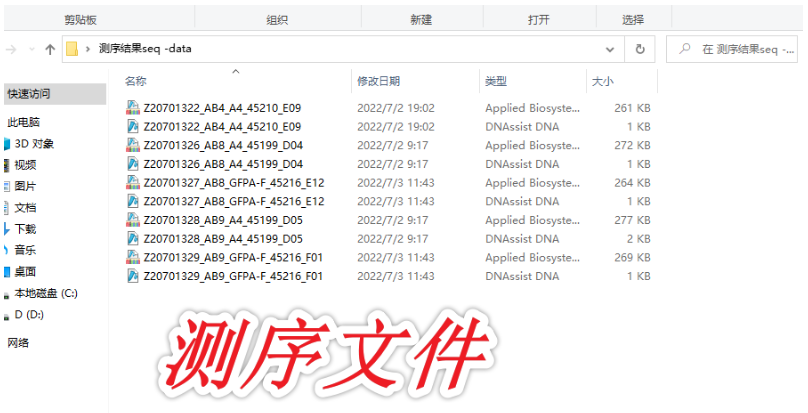
一代测序结果每个样品会有两个文件,即Applied Biosystems Sequence Trace (.ab1)和DNAssist DNA两个文件。前者有序列&峰图信息,后者只有序列信息。我们从文件大小也可以区分哪一个含的信息量更大。一般我会用大的文件进行分析,方便看峰图,因为峰图代表测序结果的质量。
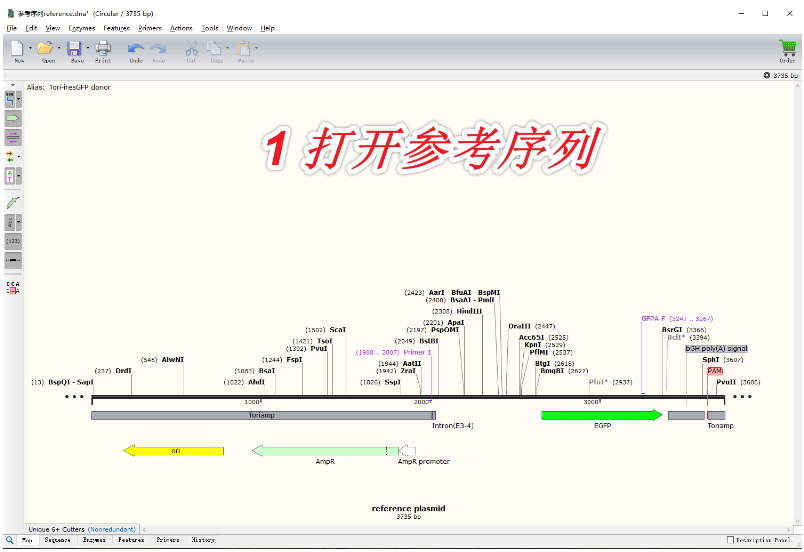
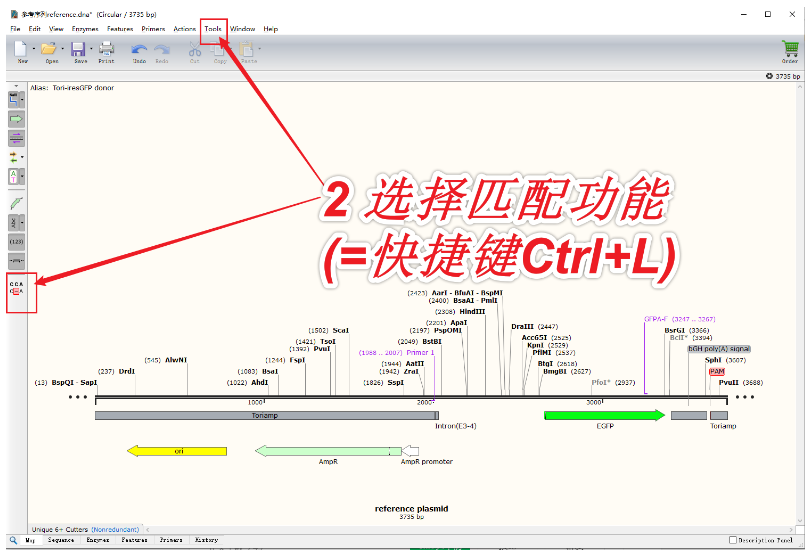
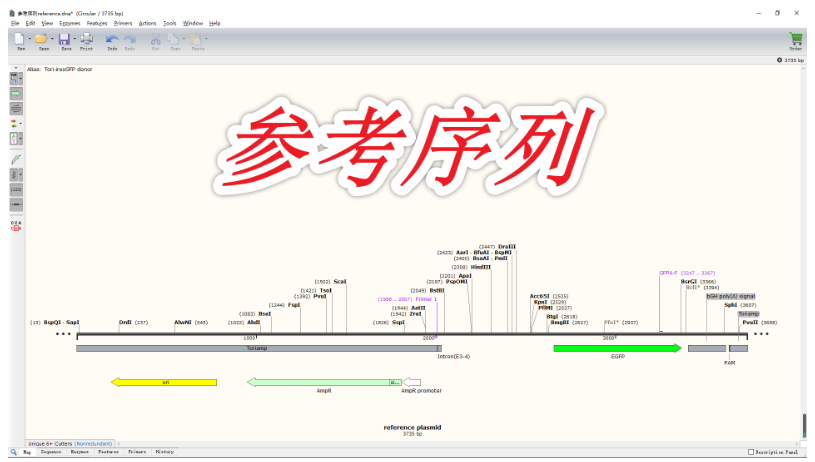
这一步有三种方法,直接按 Ctrl+L 最简单。
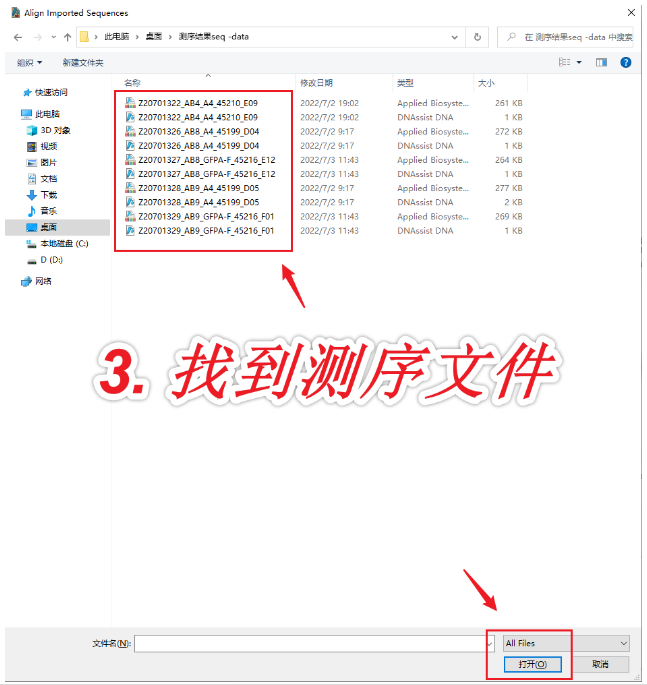
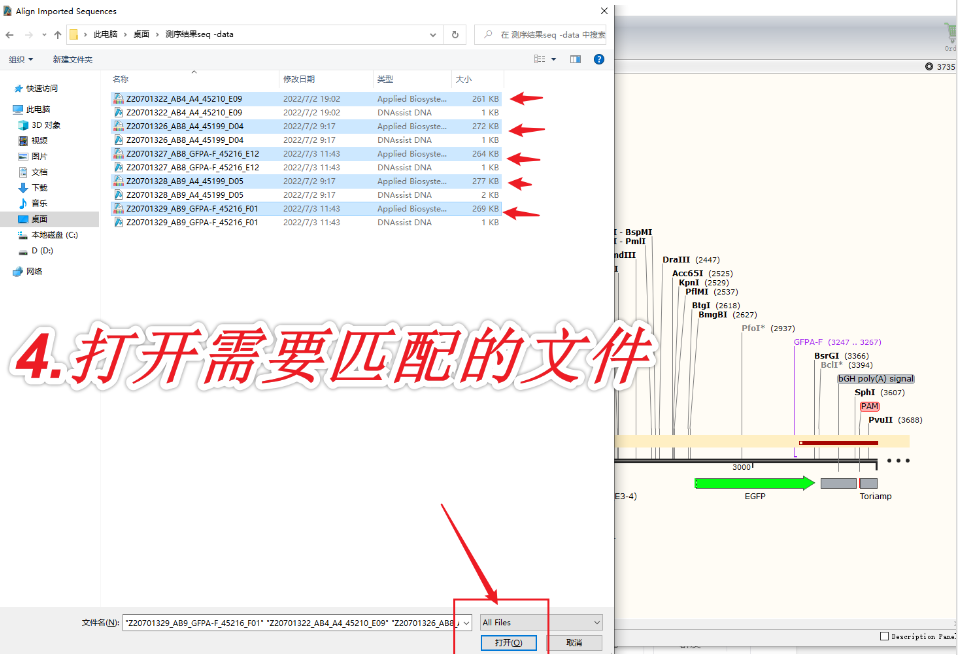
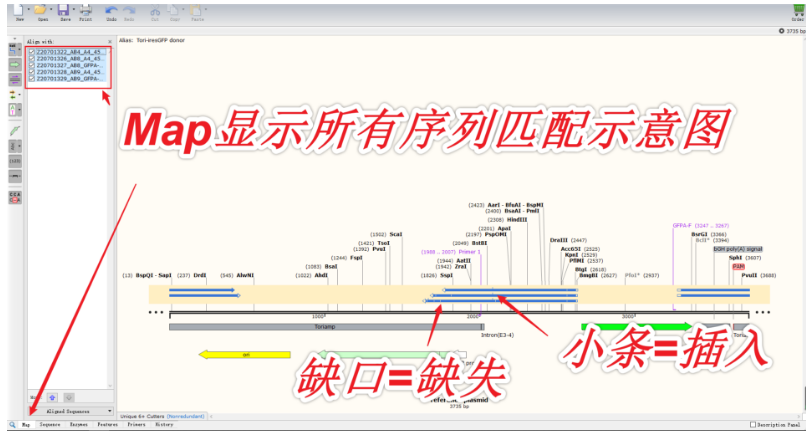

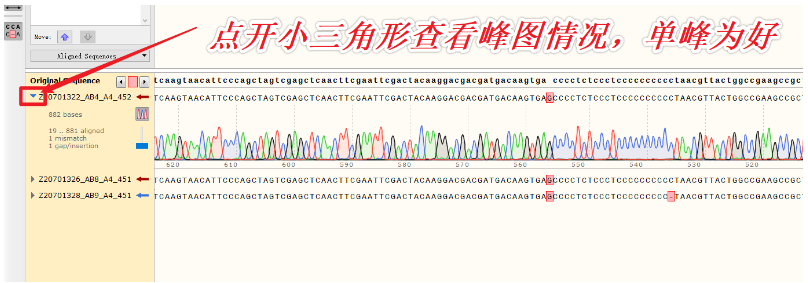
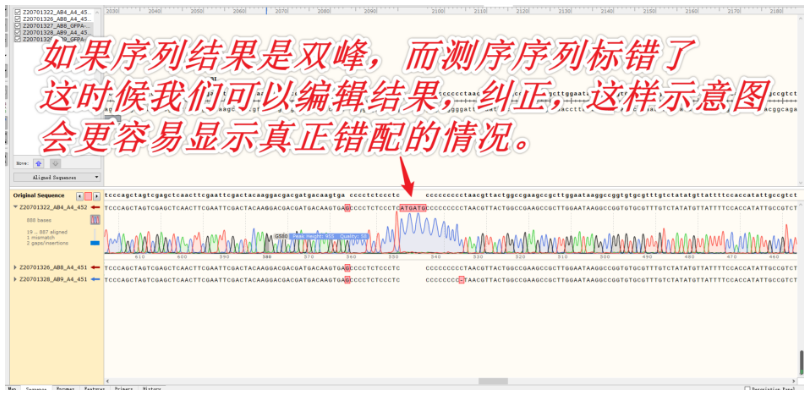
仅适用于测序结果不好的情况。
上一条:SnapGene_日常分子生物学工具
下一条:在Snapgene中去除特征